Professioneller Service Proteinidentifizierung
Proteinidentifikation
Proteinidentifizierung mittels Massenspektrometrie Die MSMS Peptid-Fragmentierungs-Fingerprint Analyse (peptide fragmentation fingerprint, PFF) liefert strukturelle Informationen zu Peptiden (AS-Sequenzen bzw. Sequence-Tags), die bei der Proteinidentifizierung über Protein- und Gen-Datenbanksuchen deutlich bessere und zuverlässigere Identifikationsergebnisse liefert als Peptidmassenfingerprint (PMF, PMM) MS-Analysen. Ferner ist PFF die Voraussetzung für die de novo Peptidsequenzierung.
Wir identifizieren und charakterisieren Ihr Protein oder Peptid:
Die Proteome Factory AG ist Ihr Dienstleister im Bereich Identifikation von Proteinen. Wir identifizieren Ihre Proteine und Peptide mittels modernster hochauflösender Massenspektrometrie (nanoLC-ESI-MSMS). Zum Einsatz kommt dabei in erster Linie nano-LC gekoppelte ESI-MS/MS. Diese Technik erlaubt die eindeutige und hochsensitive Identifikation und Charakterisierung von Proteinen und Proteingemischen. Besonders eignet sich diese Analyse für Proteinbanden oder –spots aus SDS-PAGE oder 2DE Gelen aber auch Proteingemische niedriger bis mittlerer Komplexität. Für das Protein-Profiling sehr vieler Proteinspots aus 2DE Gelen und Banden aus SDS-PAGE werden besonders attraktive Bedingungen angeboten. Neben "Standard"-Analysen werden auch spezielle MS-Analysen von Phosphoproteinen, Glykoproteinen sowie de novo Peptidsequenzierung und hochauflösende nanoLC-ESI-MS durchgeführt.
Proteine aus hochkomplexe Proben werden entweder mit eindimensionaler nano-LC-ESI-MS/MS mit Langzeitgradienten oder aber sog. MudPIT-Analysen (Multidimensional Protein Identification Technology) mit zweidimensionaler Trennung (Ionenaustausch- & RP-Chromatographie) identifiziert. Entscheidend für den eingeschlagenen Analyseweg sind in jedem Fall Ihre Bedürfnisse, wir beraten Sie gern!
Sie erhalten:
Die Ergebnisübermittlung erfolgt in der Regel elektronisch per E-mail oder über unseren gesicherten Webserver, mit Nutzername & -passwort geschütztem Bereich.
Der Report besteht aus Proteinname, Datenbanknummer, Aminosäuresequenz, Sequenzabdeckung, Molekulargewicht und dem sog. Proteinidentifizierungs-Score für das jeweilige Protein, der durch bioinformatische Algorithmen bei der Datenbanksuche berechnet wird.
Preisliste / Express-Service: Unsere Preisliste und Angaben zum Express-Service und Next-Day-Service finden Sie weiter unten. Gerne stehen wir für Ihre Beratung zur Verfügung und erstellen auf Wunsch individuelle Angebote!
Häufig gestellte Fragen zur Proteinidentifizierung wie z.B. Vermeidung von Keratin-Kontaminationen werden hier beantwortet.
Zum Probenversand empfehlen wir folgende Schritte (siehe unten).
Hochsensitive Analysendurchführung mit Qualitätssicherung
Die Durchführung der Proteinidentifizierung erfolgt unter Verwendung hoch optimierter und automatisierter Arbeitsschritte, die je nach Ihren Bedürfnissen von der elektrophoretischen Proteintrennung über das automatische Spotstanzen, den in-Gelverdau und die MS-Analyse bei Proteome Factory durchgeführt werden. Die Routineanalysen werden gemäß der SOPs in kritischen Schritten unter Reinraumbedingungen durchgeführt, um z.B. eine Kontamination mit Keratin zu verhindern, wie sie in normalen Labors häufiger auftreten können.
Die Ergebnisse der MS Standard-Analysen zur Proteinidentifizierung werden normalerweise innerhalb von 8 bis 14 Tagen nach Probeneingang per email übermittelt. Eine zeitnahere Analysendurchführung zum Identifizieren von proteinen wird durch den Express-Service und Next-Day-Service gegen Aufpreis angeboten.
Häufig gestellte Fragen zur Proteinidentifizierung
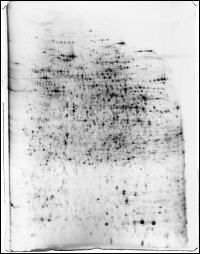
2DE-Gel mit MS kompatibler FireSilver Silberfärbung gefärbt. Das 23x30 cm große hochauflösende 2D Elektrophoresegel von 100 �g Mausnierenprobe wurde mit dem MS kompatiblen FireSilver Silberfärbungskit gefärbt. Die FireSilver Silberfärbung ist hochsensitiv mit einer Nachweisgrenze unterhalb 1ng/mm2 Protein und liefert einen sehr klaren Hintergrund (sehr gutes Signal-Rauschverhältnis). Über 2200 Proteinspots wurden in diesem Gel detektiert.
1. MS-kompatible Färbemethoden für Proteintrenngele
Als MS-verträglich für die Proteinidentifizierung sind alle Färbemethoden anzusehen, die Proteine nicht irreversibel modifizieren. Zu nennen sind in diesem Zusammenhang Coomassie Brilliant Blue CBB-R250 und CBB-G250 und Fluoreszenz-Farbstoffe wie die ready-to-use FireRuth-Fluoreszenz-Färbelösung. Sollten Sie auf hochsensitive Silberfärbung angewiesen sein, so empfehlen wir das FireSilver Gel Staining Kit. Herkömmliche Silberfärbeprotokolle und -kits verwenden in der Regel Aldehyde (Glutardialdehyd oder große Mengen an Formaldehyd), welche die Proteine irreversibel modifizieren und vernetzen. Derartig modifizierte Proteine sind aufgrund der vielfältigen Modifikationen nicht mehr zu identifizieren bzw. es wird eine erheblich größere Proteinmenge benötigt, die dann mit auch eine MS-kompatible CBB-Färbung ermöglicht.
2. Keratin und andere Kontaminationen von Proteinproben
Keratin ist der Hauptbestandteil von Haushalts- bzw. Laborstaub und kommt überall vor, wo Menschen arbeiten. Laborinstrumente und -gefäße sind aufgrund statischer Aufladung „magnetisch“ für Keratin. Wir empfehlen deshalb das gründliche Abspülen aller Geräte vor dem Kontakt mit Gelen oder anderem Probenmaterial mit 0,2 µm filtriertem Reinstwasser.
Optimalerweise arbeitet man unter einer gereinigten Cleanbench und beachte: „Steril ist nicht gleich sauber!“
Empfehlenswert ist ferner die Verwendung von (einzeln verpackten) RNAse-freien Eppendorfgefäßen, die ggf. mit 0,2 µm filtriertem Reinstwasser zuvor gespült wurden. Pipettenspitzen für die Probenahme sollten ebenfalls RNAse-frei.
Ein häufiger Kontaminationseintrag geschieht über Färbeschalen, die entweder offen (Keratin) benutzt werden oder aber vorher für immunologische Techniken (Blockieren unspezifischer Bindungen über BSA oder Milchpulver = Casein) genutzt wurden.
3. Proteinkonzentration
Die Proteinmenge sollte mind. 1 pmol pro Spezies betragen, kleinere Mengen bitte vorher absprechen, um problematische Punkte bei der Probenvorbereitung (siehe hier bei häufig gestellten Fragen) zu besprechen. Als Faustregel gilt, dass auf Coomassiegelen schwach sichtbare Spots gut identifizierbar sind. Man beachte, dass andere Färbemethoden teilweise Proteine irreversibel modifizieren und der Analyse entziehen (siehe Färbemethoden), weshalb wir unsere auf MS-Analysen optimierte Silberfärbung FireSilver empfehlen.
4. Pufferbedingungen für flüssige Proben
Für den direkten proteolytischen Verdau flüssiger Proben ist folgendes zu gewährleisten. Bei Abweichungen bitten wir Sie vorher Kontakt mit uns aufzunehmen und störende Agenzien deutlich zu vermerken.
=< 10% ACN
< 1M Harnstoff bzw. < 1M Guanidin HCl
< 0,1% SDS
< 1 mM DTT
- keine Proteaseinhibitoren
- der pH-Wert sollte möglichst im neutralen bis leicht alkalischen Bereich
- die Ionenstärke sollte nicht 150mM übersteigen
5. Proteasen
Neben Trypsin können auch andere Spaltenzyme oder –agenzien eingesetzt werden, dies in der Regel gegen Aufpreis:
- Asp-N Protease
- Glu-C Protease
- Lys-C Protease
- Arg-C Protease
- Pepsin
- Bromcyan
- NTCB
- Iodosobenzoesäure
- Ameisensäure
- Thermolysin
- Chymotrypsin
- Proteinase K
Probenversand
- Füllen Sie unser MS-Probenformular für die Protein Identifikation (pdf, 233 kB) mit Informationen über die Proben aus (z.B. Probename, Probentyp, MW, Proteinmenge, Färbungsmethode).
- Unterzeichnen Sie das Formular.
- Informieren Sie uns per E-mail oder telefonisch, dass Sie Ihre Proben an uns schicken.
- Füllen Sie Ihre Proben in zuvor mit 0,2 µm filtriertem Reinstwasser gespülte Eppendorf-Reaktionsgefäße, die Sie mit Parafilm umwickeln.
- Proteinspots und Proteingelbanden sollten nach dem Ausstanzen ohne zusätzlich Flüssigkeit in die Eppis transferiert werden.
- Proteinproben auf PVDF-Membran können Sie entweder als ausgeschnittene Proteinbande trockenen im Eppi an uns schicken oder als angefärbte getrocknete PVDF-Membran in einer Plastikhülle mit beiliegender Beschreibung/Beschriftung der zu analysierenden Proteinbande.
- Flüssige Proben versenden Sie bitte im gefrorenen Zustand. Bitte klären Sie vorab mit dem Transportunternehmen, ob diese Trockeneis (=Gefahrgut!) befördern.
- Lyophilisierte oder im Gel befindliche Proben können in der Regel ungekühlt verschickt werden.
- Schicken Sie bitte Ihre Proben in einem wattierten Briefumschlag oder einem Päckchen zusammen mit dem Probenformular an uns:
Versandadresse
Proteome Factory AG
Magnusstr. 11
DE-12489 Berlin
Datenschutz und Geheimhaltung
Die Proteome Factory AG nimmt den Schutz Ihrer Daten sehr ernst. Diese werden deshalb nur intern verarbeitet und sind nur den beteiligten Mitarbeitern zugänglich. Die Kommunikation und Ergebnisübermittlung erfolgt auf Wunsch mittels etablierter Sicherungs- und Verschlüsselungstechnik. Ferner werden Ihre Daten redundant und ausfallsicher gespeichert.
Auf Wunsch treffen wir mit Ihnen eine schriftliche Geheimhaltungsvereinbarung.
Express-Service
Express-Service: nanoLC-ESI-MSMS Analyse innerhalb 3-4 Werktagen
Für die nanoLC-ESI-MSMS Analysen wird ein Express-Service mit einer beschleunigten Analysendurchführung innerhalb von 3-7 Tagen nach Probeneingang angeboten. Wir berechnen einen Aufpreis von 50% auf die Standardanalyse.
Next-Day-Service: nanoLC-ESI-MSMS Analyse zur Proteinidentifizierung innerhalb eines Tages
Für die nanoLC-ESI-MSMS Analysen wird ein Next-Day-Service mit einer beschleunigten Analysendurchführung bis zum Ende des nächsten Tages nach Probeneingang angeboten. Der Probeneingang muß an einem Werktag bis 12 Uhr mittags erfolgen. Wir empfehlen für dieses Angebot einen über Nacht Expressversand der Proben mit garantierter Anlieferung am Vormittag. Ein Aufschlag von 100% auf den Standardanalysenpreis wird berechnet.
Hochauflösende Massenspektrometrie (nanoLC-ESI-MSMS)
(gültig ab 1. Oktober 2023)
Proteinidentifizierung mit nanoLC-ESI-MSMS
Hochsensitive Proteinidentifizierung mittels nanoLC-ESI-MSMS. Sehr gut geeignet für Proteinbanden aus PAGE Gelen, Proteinspots aus 2DE Gelen und einfache Proteingemische. Durch die nanoLC-Trennung mit online-gekoppelter nano-ESI-MSMS können meist mehr Peptide während der Proteinidentifizierung analysiert und fragmentiert werden als bei MALDI-TOFTOF-MS Analysen ohne chromatographische Trennung. Dadurch wird meistens eine bessere und eindeutigere Proteinidentifikation mit höherem Identifizierungs-Score bei der Datenbanksuche erzielt. Standardmäßig erfolgt eine Datenbanksuche gegen die NCBInr Proteindatenbank. Auf Anfrage können auch andere Datenbanken gegen Aufpreis eingesetzt werden.
Proteinidentifizierung - Preise für Europa
Protein-Identifizierung mit |
Preis pro Probe [EUR] im
Standard-Service (1-2 Wochen) |
||
| Proben mit 1-10 Proteinen (kurzer LCMS-Gradient, f�r PAGE-Banden und 2DE-Spots) | Proben mit mittlerer Komplexit�t oder gel�ste Proteine (normaler LCMS-Gradient) | komplexe Proben mit vielen Proteinen bzw großem dynamischen Bereich (langer LCMS-Gradient) | |
| 1 Probe | 300 | 550 | 850 |
| 2 - 9 Proben | 250 | 500 | 750 |
| 10 - 24 Proben | 225 | 450 | 650 |
| 25 und mehr Proben | auf Anfrage | auf Anfrage | auf Anfrage |
| Express Service (3-4 Tage) | +50% | ||
| Next-Day Service (Über Nacht) | +100% |
Zusatz-Services für die Protein-Identifizierung
LCMS-basierte Proteomik, Quantitiative Proteomik
| Preis pro Probe [EURO] |
|
| iTRAQ-basierte Proteomics-Quantifizierung | auf Anfrage |
| MudPIT Proteomics | auf Anfrage |
nanoLC-ESI-MSMS-basierte Proteomik mit |
auf Anfrage |
Protein Profiling aus 2DE Gelen
nanoLC-ESI-MSMS Protein Profiling aus 2DE Gelen
Die Proteinprofilierung aus 2DE Gelen wird mit nanoLC-ESI-MSMS durchgeführt, die eine hochsensitive Proteinidentifikation sicherstellt. Zuvor werden die Proteinspots automatisch mit dem Hochdurchsatz Spotpicker spotXpress nach Kundenliste ausgestanzt und unter Einsatz des Probenvorbereitungsroboters SpotDigest 96 für die Proteinidentifizierung effektiv vorbereitet, wodurch eine kontaminationsfreie Arbeitsweise ermöglicht wird. Die Auswertung und Datenbanksuche der nanoLC-ESI-MSMS Analysen erfolgt automatisch. Die Ergebnisse der Proteinidentifizierung werden auf elektronischem Weg dem Kunden zugesandt.
|
ab 50. Proteinspots: 150 EURO* pro Proteinspot ab 100. Proteinspots: 100 EURO* pro Proteinspot |
*Alle Preise verstehen sich zzgl. 19% Mehrwertsteuer.
** Im Fall einer nicht erfolgreichen Phosphoprotein- oder Glykoproteinanalyse, d.h. keiner Identifizierung einer oder mehrere Modifikationsstellen, wird der Standardpreis für eine nanoLC-ESI-MSMS Analyse berechnet.